Os vírus penetram nas células humanas de forma muito eficiente, principalmente graças a proteínas especializadas que cobrem as suas superfícies externas. Estas proteínas são alvos chave no desenvolvimento de vacinas. Para estudá-los, os cientistas geralmente criam versões de laboratório para ver como o sistema imunológico pode reagir. No entanto, estas versões simplificadas muitas vezes carecem de regiões importantes que normalmente são encontradas dentro da membrana externa do vírus. Como resultado, nem sempre se comportam como numa infecção real, tornando mais difícil compreender como os anticorpos realmente reconhecem e detêm os vírus.
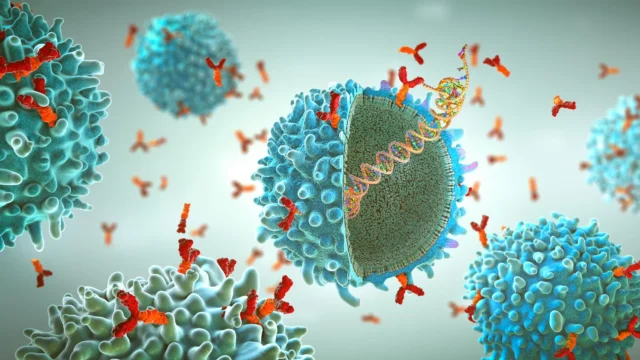
Os investigadores da Scripps Research, trabalhando com a IAVI e outros, desenvolveram agora uma nova plataforma que lhes permite estudar estas proteínas virais de uma forma muito mais natural. Seu método usa tecnologia de nanodiscos, que encapsula proteínas em minúsculas partículas lipídicas. Esta configuração imita a membrana externa do vírus, ajudando a preservar a estrutura natural e o comportamento das proteínas. Esta abordagem oferece uma imagem mais clara de como os anticorpos interagem com os vírus e pode ajudar no desenvolvimento de uma futura vacina.
Tecnologia Nanodisc imita membranas virais
Um estudo publicado em Comunicações da naturezatestou a plataforma usando proteínas do HIV e do Ebola. Esses vírus há muito representam desafios para o desenvolvimento de vacinas porque suas proteínas de superfície são particularmente difíceis de serem atingidas pelo sistema imunológico. Os investigadores acreditam que o mesmo método pode ser aplicado a outros vírus com proteínas ligadas à membrana semelhantes, incluindo a gripe e o SARS-CoV-2.
“Durante anos, tivemos que confiar em versões de proteínas virais que careciam de partes importantes”, diz o co-autor William Schiff, professor da Scripps Research e diretor executivo de desenvolvimento de vacinas no IAVI Center for Neutralizing Antibodies. “Nossa plataforma nos permite estudar essas proteínas em condições que refletem melhor seu ambiente natural, o que é fundamental se quisermos entender como os anticorpos protetores reconhecem o vírus”.
Em vírus reais, as proteínas de superfície estão incorporadas na membrana lipídica e organizadas em determinados formatos. Por outro lado, a maioria dos estudos de laboratório remove a parte que ancora a membrana para facilitar o trabalho com as proteínas. Embora isto simplifique as experiências, pode obscurecer detalhes importantes, especialmente para anticorpos que têm como alvo regiões próximas da base da proteína perto da membrana.
Para superar esta limitação, a equipe incorporou proteínas candidatas a vacina nos nanodiscos. Essas pequenas e estáveis placas lipídicas mantêm as proteínas no lugar e se assemelham muito à camada externa de um vírus. Esta configuração permite aos cientistas estudar como os anticorpos interagem com as proteínas num contexto mais realista. A plataforma também oferece suporte a ferramentas padrão de pesquisa de vacinas, incluindo ensaios de ligação de anticorpos, classificação de células imunológicas e imagens de alta resolução.
“O principal foi combinar todos esses componentes em um único sistema robusto”, diz a primeira autora Kima Rantolainen, cientista sênior do laboratório de Schiff. “As peças individuais já existiam, mas fazê-las funcionar em conjunto de uma forma reproduzível e escalável abre novas oportunidades para análise e desenvolvimento de vacinas”.
Novos insights sobre a resposta de anticorpos
Usando o VIH como exemplo, os investigadores concentraram-se numa região estável da proteína da superfície do vírus localizada junto à membrana. Esta região é alvo de um grupo de anticorpos que podem bloquear uma ampla gama de variantes do HIV. Estes anticorpos reconhecem partes do vírus que permanecem consistentes mesmo quando sofre mutação, o que os torna particularmente valiosos para a investigação de vacinas.
Usando a plataforma nanodisc, a equipe capturou visões estruturais detalhadas de como esses anticorpos interagem com proteínas virais em seu ambiente de membrana nativo. Isto revelou características que não podem ser observadas quando as proteínas são estudadas isoladamente. As descobertas também esclarecem como certos anticorpos podem neutralizar os vírus, destruindo as estruturas que utilizam para infectar as células, oferecendo pistas úteis para a concepção de melhores vacinas.
“A estrutura nos deu um nível de detalhe que simplesmente não conseguíamos acessar antes”, observa Rantolainen. “Isso nos mostrou novas interações na interface da membrana e sugeriu por que elas são importantes para a função dos anticorpos”.
Aplicações além de HIV e Ebola
Para mostrar que o método é amplamente útil, os investigadores também o aplicaram às proteínas do Ébola. Os resultados confirmaram que os anticorpos podem reconhecer e ligar-se com sucesso a estas proteínas no mesmo ambiente semelhante a uma membrana.
A plataforma não se limita à análise estrutural. Também pode ser usado para estudar respostas imunológicas a vacinas candidatas. Usando os nanodiscos como “isca” molecular, os cientistas podem isolar células do sistema imunológico que respondem a proteínas virais específicas. Isto proporciona uma melhor compreensão de como o corpo responde a diferentes designs de vacinas. Além disso, o sistema é eficiente. Processos que costumavam levar um mês ou mais agora podem ser concluídos em cerca de uma semana, facilitando a comparação de múltiplas vacinas candidatas.
Uma ferramenta para acelerar o desenvolvimento de vacinas
Embora a plataforma em si não seja uma vacina, ela serve como uma ferramenta poderosa para apoiar a investigação de vacinas. Isto é especialmente importante para vírus que têm sido difíceis de corrigir usando métodos tradicionais.
“Isso dá ao campo uma maneira mais realista e precisa de testar ideias numa fase inicial”, enfatiza Schiff. “Ao melhorar a forma como estudamos as proteínas virais e as respostas dos anticorpos, esperamos que esta plataforma ajude a desenvolver vacinas de próxima geração contra alguns dos vírus mais desafiadores do mundo”.
Além de Schiff e Rantolainen, os autores da Plataforma de Nanodiscos de Glicoproteína Viral para Análise de Vacinas incluem Alessia Liguori, Gabriel Azarovsky, Claudia Flynn, John M. Steichen, Olivia M. Swanson, Patrick J. Madden, Sabyasachi Babu, Swastik Phulera, Anant Harpur, Danny Lu, Alexander Kalyuzhny, Patrick Skog, Sierra Terada, Manalina Shil, Jolene K. Diedrich, Eric Georgeson, Ryan Tingle, Saman Eskandarzadeh, Wen-Xin Lee, Nushin Alavi, Diana Goodwin, Michael Kubitz, Sonia Amirzehni, Devin Sock, Jung Hyun Lee, John R. Yates III, James S. Paulson, Shane Crotty, Torben Schiffner e Andrew B. Ward of Scripps Research; e Sunny Hymansu da Moderna Inc.
Este trabalho foi apoiado por financiamento do Instituto Nacional de Alergia e Doenças Infecciosas dos Institutos Nacionais de Saúde (subsídios UM1 AI144462, R01 AI147826, R56 AI192143 e 5F31AI179426-02); Colaboração da Fundação Bill & Melinda Gates para a descoberta de vacinas contra a AIDS (concede INV-007522, INV-008813 e INV-002916); Centro de Anticorpos Neutralizantes IAVI (INV-034657 e INV-064772); e a Fundação Alexander von Humboldt.